-
下表为常用的限制性核酸内切酶及其识别序列和切割位点(注:表中Y为C或T,R为A或G)。据表分析,可以得到的结论是( )
限制酶名称
识别序列和
切割位点
限制酶名称
识别序列和
切割位点
BamHⅠ
G↓GATCC
KpnⅠ
GGTAC↓C
EcoRⅠ
G↓AATTC
Sau3AⅠ
↓GATC
HindⅡ
GTY↓RAC
SmaⅠ
CCC↓GGG
A.限制酶的切割位点在识别序列的中间
B.限制酶切割后都形成黏性末端
C.不同限制酶切割后形成的黏性末端都相同
D.一种限制酶可能识别多种核苷酸序列
高三生物选择题中等难度题查看答案及解析
-
下表为常用的限制性核酸内切酶及其识别序列和切割位点(注:表中Y为C或T,R为A或G)。据表分析,可以得到的结论是( )
限制酶名称
识别序列和切割位点
限制酶名称
识别序列和切割位点
BamHⅠ
G↓GATCC
KpnⅠ
GGTAC↓C
EcoRⅠ
G↓AATTC
Sau3AⅠ
↓GATC
HindⅡ
GTY↓RAC
SmaⅠ
CCC↓GGG
A.限制酶的切割位点在识别序列的中间
B.限制酶切割后都形成黏性末端
C.不同限制酶切割后形成的黏性末端都相同
D.一种限制酶可能识别多种核苷酸序列
高三生物选择题中等难度题查看答案及解析
-
下表为常用的限制性核酸内切酶及其识别序列和切割位点(注:表中Y为C或T,R为A或G)。据表分析,可以得到的结论是( )

A.限制酶的切割位点在识别序列的中间
B.限制酶切割后都形成黏性末端
C.不同限制酶切割后形成的黏性末端都相同
D.一种限制酶可能识别多种核苷酸序列
高三生物选择题中等难度题查看答案及解析
-
下表为常用的限制性核酸内切酶(限制酶)及其识别序列和切割位点,由此推断的以下说法
正确的是( )
限制酶名称
识别序列和切割位点
限制酶名称
识别序列和切割位点
BamHⅠ
G↓GATCC
KpnⅠ
GGTAC↓C
EcoRⅠ
C↓AATTC
Sau3AⅠ
↓GATC
HindⅡ
GTY↓RAC
SmaⅠ
CCC↓GGG
(注:Y=C或T,R=A或G)
A.限制酶切割后不一定形成黏性末端
B.限制酶的切割位点一定在识别序列的内部
C.不同限制酶切割后一定形成不同的黏性末端
D.一种限制酶一定只能识别一种核苷酸序列
高三生物综合题中等难度题查看答案及解析
-
下表为常用的限制性核酸内切酶(限制酶)及其识别序列和切割位点,由此推断的以下说法中,正确的是
限制酶名称
识别序列和切割位点
限制酶名称
识别序列和切割位点
BamHⅠ
G↓GATCC
KpnⅠ
GGTAC↓C
EcoRⅠ
C↓AATTC
Sau3AⅠ
↓GATC
HindⅡ
GTY↓RAC
SmaⅠ
CCC↓GGG
(注:Y=C或T,R=A或G)
A.一种限制酶只能识别一种核苷酸序列
B.限制酶切割后一定形成黏性末端
C.不同的限制酶可以形成相同的黏性末端
D.限制酶的切割位点在识别序列内部
高三生物选择题中等难度题查看答案及解析
-
下表为常用的限制性核酸内切酶(限制酶)及其识别序列和切割位点,由此推断的以下说法中,正确的是
限制酶名称
识别序列和切割位点
限制酶名称
识别序列和切割位点
BamHⅠ
G↓GATCC
KpnⅠ
GGTAC↓C
EcoRⅠ
C↓AATTC
Sau3AⅠ
↓GATC
HindⅡ
GTY↓RAC
SmaⅠ
CCC↓GGG
(注:Y=C或T,R=A或G)
A.一种限制酶只能识别一种核苷酸序列
B.限制酶切割后一定形成黏性末端
C.不同的限制酶可以形成相同的黏性末端
D.限制酶的切割位点在识别序列内部
高三生物选择题中等难度题查看答案及解析
-
下表为常用的限制性核酸内切酶(限制酶)及其识别序列和切割位点,由此推断以下说法中,正确的是( )
制酶名称
识别序列和切割位点
限制酶名称
识别序列和切割位点
BamHⅠ
G↓GATCC
KpnⅠ
GGTAC↓C
EcoRⅠ
C↓AATTC
Sau3AⅠ
↓GATC
HindⅡ
GTY↓RAC
SmaⅠ
CCC↓GGG
(注:Y=C或T,R=A或G)
A.限制酶切割后不一定形成黏性末端
B.限制酶的切割位点在识别序列的内部
C.不同限制酶切割后一定形成不同的黏性末端
D.一种限制酶一定只能识别一种核苷酸序列
高三生物单选题中等难度题查看答案及解析
-
下表为常用的限制性核酸内切酶及其识別序列和切割位点,有关说法正确的是
限制性核
酸内切酶
识别序列和
切割位点
限制性核酸
内切酶
识别序列和切
割位点
BamHⅠ
G↓GATCC
KpnⅠ
GGTAC↓C
EcoRⅠ
G↓AATTC
Sau3AⅠ
↓GATC
HindⅡ
GTY↓RAC
SmaⅠ
CCC↓GGG
(注:Y表示C或T,R表示A或G)
A. 限制性核酸内切酶的切点位于识别序列的内部
B. 限制性核酸内切酶切割后不一定形成黏性末端
C. 种限制性核酸内切酶只能识别一种脱氧核苷酸序列
D. 不同限制性核酸内切酶切剂后一定形成不同的黏性末端
高三生物单选题中等难度题查看答案及解析
-
某线性DNA分子含有5000个碱基对(bp),先用限制性核酸内切酶a完全切割,再把得到的产物用限制性核酸内切酶b完全切割,得到的DNA片段大小如下表。限制性核酸内切酶a和b的识别序列和切割位点如下图所示。下列有关叙述错误的是
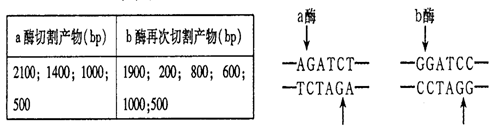
A.a酶与b酶切断的化学键相同
B.限制性核酸内切酶a和b切出的DNA片段不能相互连接
C.该DNA分子中a酶能识别的碱基序列有3个
D.仅用b酶切割该DNA分子至少可得到三种DNA片段
高三生物选择题中等难度题查看答案及解析
-
某线性DNA分子含有5000个碱基对(bp),先用限制性核酸内切酶a完全切割,再把得到的产物用限制性核酸内切酶b完全切割,得到的DNA片段大小如下表。限制性核酸内切酶a和b的识别序列和切割位点如下图所示。下列有关叙述错误的是
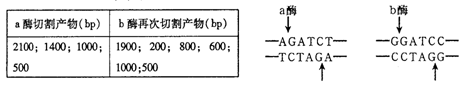
A.a酶与b酶切断的化学键相同
B.限制性核酸内切酶a和b切出的DNA片段不能相互连接
C.该DNA分子中a酶能识别的碱基序列有3个
D.仅用b酶切割该DNA分子至少可得到三种DNA片段
高三生物选择题中等难度题查看答案及解析